丰培强研究组合作建立基于结构的植物蛋白功能注释新方法并鉴定新型过氧化物酶体发生因子
2026年2月9日(北京时间),国际知名学术期刊 ThePlant Cell 以Breakthrough Report形式在线发表了中国科学院分子植物科学卓越创新中心丰培强研究组与浙江大学潘荣辉、沈星星研究组合作完成的题为 “Structure-guided discovery of novel protein functions in plants” 的研究论文。该文章通过对17个被子植物全蛋白质组的结构聚类与深度挖掘,建立了一套高效的“结构同源-功能保守”预测方法,不仅系统地注释了之前未被注释的植物蛋白,预测了它们的功能;并且通过这个方法鉴定出新的植物过氧化物酶体发生因子PEX8,揭示了其在过氧化物酶体生物发生过程中的作用。
基因组测序时代留下的最大挑战之一是“暗物质”蛋白——即那些因序列高度变异而无法通过传统的序列比对工具找到同源物的蛋白,在植物中这一比例往往高达20%-30%,基于序列的方法往往难以识别其远缘同源关系从而限制了对蛋白功能谱系和生物学意义的全面理解。为了解决这个问题,研究团队建立了一套“结构预测-聚类-减法筛选-功能验证”的闭环体系,有效地利用结构保守性跨越了蛋白序列演化上的鸿沟。不同于以往局限于单一物种或特定家族的研究,该工作通过整合公共数据库中已有的蛋白结构数据,利用AlphaFold2等结构预测工具对来自17个代表性被子植物(涵盖基部被子植物、单子叶与真双子叶植物)的蛋白进行结构预测,构建了一个包含约56万个蛋白结构的综合数据集。随后团队利用FoldSeek对蛋白结构进行聚类分析,结合结构预测置信度的打分分布,筛选到那些序列同源性低,但在三维结构上高度保守的蛋白结构簇,进行后续分析。该研究建立了一套高效的蛋白筛选流程,剔除了那些可以通过BLAST序列比对找到同源物的案例,通过“结构比对阳性”而“序列比对阴性”的差异化筛选,锁定了3,109个主要依赖结构维系功能的候选簇,从而确保了发现的“净增量”和新颖性。在自动化筛选流程之外,团队成员还引入了对Swiss-Prot、TAIR、eggNOG及HHblits等多个数据库的交叉验证,通过多重过滤,最终确定了120个高度保守且功能未知的蛋白质簇。据此,该研究建立了首个植物中系统性的蛋白结构基因组学研究范式,为解析植物蛋白功能与演化提供重要的参考依据。
为了进一步验证这些结构簇所蕴含的生物学功能,研究团队通过与功能已知的蛋白结构库进行系统比对,成功揭示了大部分的结构簇获得了精准的功能注释,其中一项重要的成果是发现了一个新的植物过氧化物酶体生物发生因子PEX8。
过氧化物酶体是真核生物中高度保守的细胞器,主要参与胞内的脂肪酸代谢和活性氧清除。此外,植物中过氧化物酶体还广泛参与激素合成、乙醛酸循环和光呼吸途径等,对植物的生长发育和逆境适应性具有关键作用。PEX8是酵母中保守的过氧化物酶体生物发生因子,但是由于序列同源性低,植物中相对应的同源蛋白长期未被鉴定,导致该领域的研究人员一直认为植物中并不存在PEX8。研究团队通过结构比对发现,拟南芥Cluster_10847虽然与酵母PEX8序列相似度极低,但结构高度同源,并且都具有典型的过氧化物酶体定位信号肽PTS1。基于此线索,团队还鉴定到了水稻等其他植物物种的同源蛋白。遗传实验表明拟南芥PEX8敲除突变体具有胚胎致死的表型,这与其他PEX成员是一致的。随后,团队不仅通过实验验证了其过氧化物酶体的定位,揭示了植物PEX8保留了酵母PEX8独特的“PTS1非依赖性”定位机制;而且还通过遗传互补实验,证明了拟南芥、水稻和苔藓的PEX8能互补酵母PEX8缺失突变体的表型。
综合上述结构分析与功能实验结果可以看出,植物的PEX8与酵母的PEX8在功能上具有一致性,参与过氧化物酶体的生物发生。尽管历经亿万年的序列变异,其核心的生化功能骨架依然保守。这一发现不仅找到了植物过氧化物酶体发生长期缺失的一个关键组分,也展示了结构导向方法在揭示古老细胞器起源与进化中的独特优势。此外,本研究的结果表明部分植物蛋白的结构直接指向蓝细菌,为叶绿体的内共生起源提供了“结构化石”般的证据。同时,研究揭示了同一物种内存在“结构相似但序列迥异”的基因对,这提示了基因复制后,为了适应复杂环境,植物基因组在保留核心结构功能的同时,可能经历了极高强度的序列演化选择。
该项工作是“AI for Science”在植物学领域的应用案例,表明了蛋白质结构数据库不再仅仅是结构生物学家的参考书,而是功能基因组学研究的丰富资源库。该研究所提供的120个高置信度功能簇,以及经过验证的PEX8案例,为未来的作物遗传改良、合成生物学元件挖掘以及基础生命过程解析提供了宝贵资源和新思路。
鉴于该研究的创新性和重要意义,The Plant Cell同期发表了题为“Beyond sequences: Structure-guided discovery of novel protein functions in plants“的评论型文章,对该研究进行了解读和评价。
浙江大学博士生陈佳荣 、副研究员冯彦磊、博士生张钰婵(已毕业)和博士后高炬灿(现为浙江理工大学副研究员)为该论文的共同第一作者,分子植物科学卓越创新中心一年级博士生区晋达参与了该项工作。浙江大学农业与生物技术学院潘荣辉教授、浙江大学沈星星教授和分子植物科学卓越创新中心丰培强研究员为该论文共同通讯作者。该研究得到中国科学院分子植物科学卓越创新中心、中国科学院上海分院的支持和资助。
论文链接:https://doi.org/10.1093/plcell/koag022
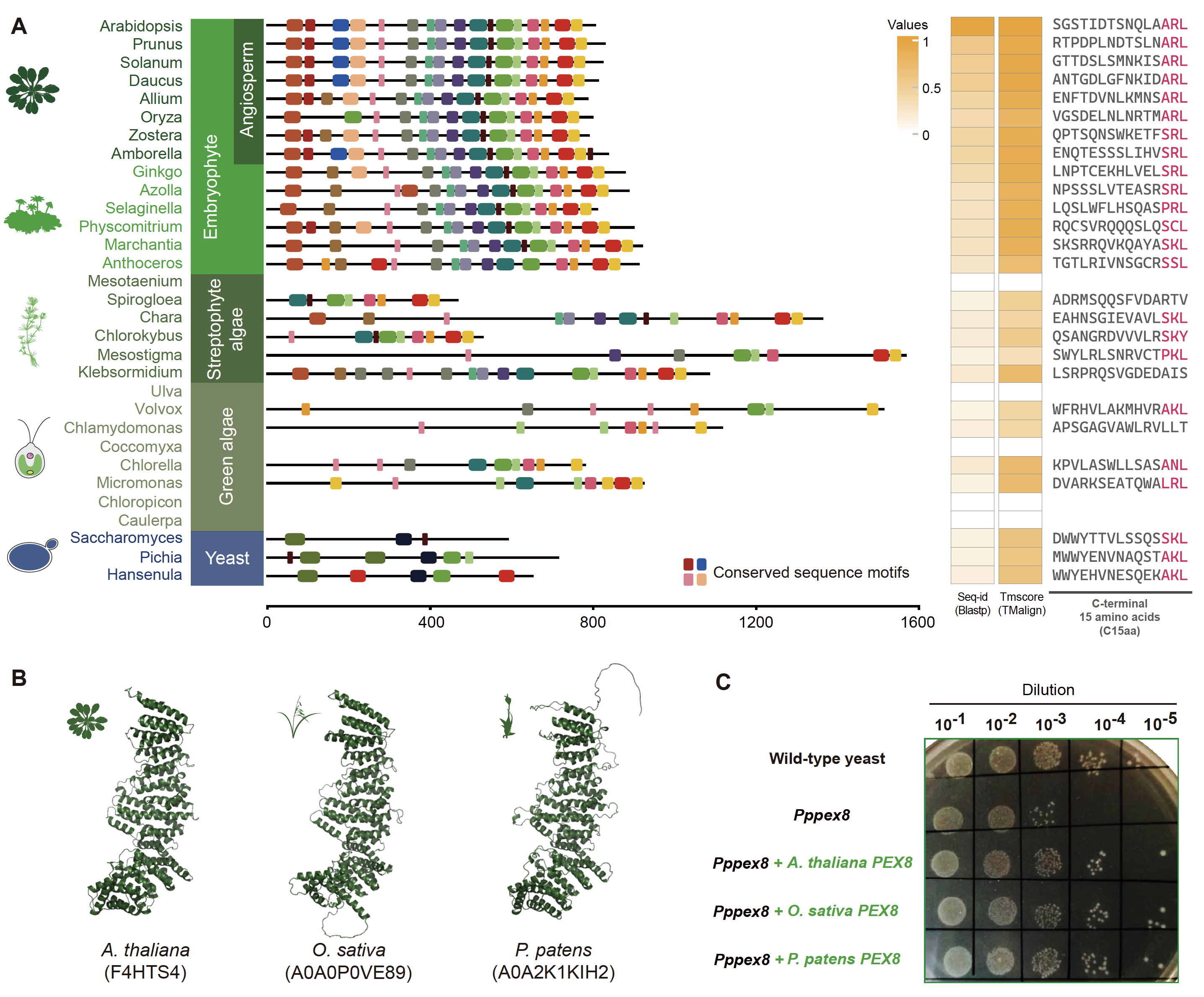
图1 植物PEX8蛋白的结构保守性及其功能验证